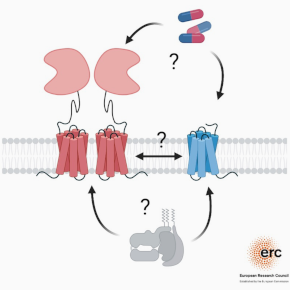
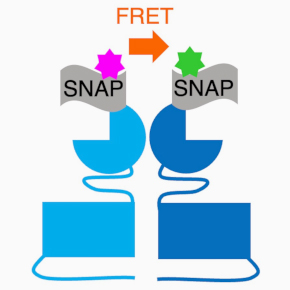
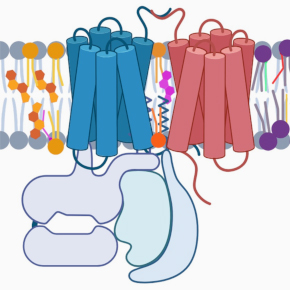
Les récepteurs mGlu et GABA-B sont des récepteurs couplés aux protéines G complexes qui fonctionnent sous la forme d’homodimères ou d’hétérodimères. Ils sont également capables de former des complexes avec d’autres protéines, y compris des protéines membranaires, pour moduler leur activité in vivo. Il est important de mieux comprendre les bases moléculaires et structurales de ces complexes et leur dynamique, en particulier pour développer de nouvelles molécules d’intérêt thérapeutique dans le domaine des maladies neurologiques et psychiatriques.
Le projet de recherche de l’équipe a quatre objectifs spécifiques :
1 – Étudier les bases moléculaires et structurales des récepteurs mGlu et des complexes qu’ils forment avec d’autres partenaires membranaires, par des approches biophysiques et structurales (cryo-électron microscopie, analyse de la dynamique conformationnelle à l’échelle de la molécule unique par la technique de transfert d’énergie de résonance de type Förster ou FRET).
2- Développer des méthodes et des outils pour l’étude des récepteurs mGlu et GABA-B in vitro et dans leur environnement natif. Les méthodes privilégiées sont des biosenseurs basés sur les technologies de transfert d’énergie de résonance de type Förster (FRET, HTRF®) ou de bioluminescence (BRET). Les outils développés sont des ligands spécifiques, des petites molécules ou des anticorps de camélidés (nanobodies), et certains d’entre eux sont contrôlables par la lumière.
3- Étudier les complexes formés par les récepteurs mGlu et leur dynamique dans leur environnement natif. L’objectif est d’identifier des complexes fonctionnels dans le cerveau, tels que les récepteurs mGlu hétérodimériques que l’équipe a récemment découverts. Et de comprendre l’importance physiologique de ces complexes pour le fonctionnement des neurones et du cerveau. Les outils décrits ci-dessus sont utilisés.
4 – Développer les nanobodies ciblant les récepteurs mGlu comme immunothérapie innovante pour le traitement de maladies du cerveau, en particulier la schizophrénie.
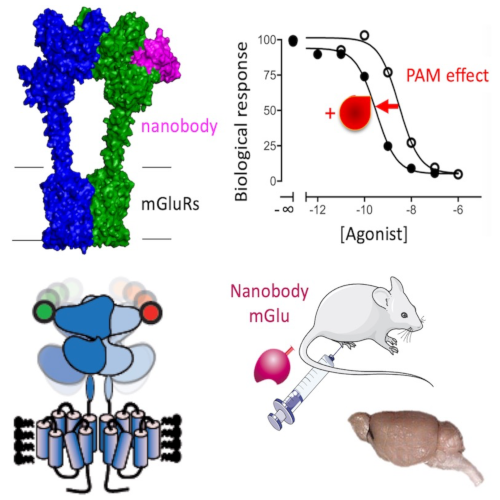
L’équipe étude la pharmacologie moléculaire des récepteurs mGlu et GABA-B, depuis leur structure et leur mécanisme d’activation, leur pharmacologie et leur signalisation, jusqu’au développement de nouveaux ligands innovants (mini-anticorps de camélidés et composés photo-activables) et à leurs applications dans plusieurs modèles de maladies du cerveau.
Chef d'équipe

DR1, Inserm

IGF Nord 223

04 34 35 92 89
En savoir plus >
Chercheurs

CRCN, CNRS

IGF Nord 209b

04 34 35 92 78
En savoir plus >

DRCE, CNRS

IGF Nord 223

04 34 35 92 89
En savoir plus >

DR2, CNRS

IGF Nord 221a

04 34 35 93 07
En savoir plus >

Accueil scientifique, CNRS

IGF Nord 221a

04 34 35 93 07
En savoir plus >
Techniciens et ingénieurs

IEHC, CNRS

IGF Nord 219

04 34 35 93 13
En savoir plus >

IECN, CNRS

IGF Nord 221a

04 34 35 93 07
En savoir plus >
Chercheurs CDD et doctorants

Doctorant(e), UM

IGF Nord 223

04 34 35 93 07
En savoir plus >

Chercheur CDD, CNRS

IGF Nord 215a

04 34 35 93 07
En savoir plus >

Chercheur CDD, CNRS

IGF Nord 221a

04 34 35 93 07
En savoir plus >

Chercheur CDD, CNRS

IGF Nord 223

04 34 35 92 78
En savoir plus >

Doctorant(e), UM

IGF Nord 221a

04 34 35 92 78
En savoir plus >

Chercheur CDD, CNRS

IGF Nord 209b

04 34 35 93 07
En savoir plus >

Chercheur CDD, CNRS

IGF Nord 209b

04 34 35 92 89
En savoir plus >

Chercheur CDD, CNRS

IGF Nord 223

04 34 35 92 89
En savoir plus >

Chercheur CDD, CNRS

IGF Nord 216a

04 34 35 92 63
En savoir plus >

Chercheur CDD, CNRS

IGF Nord 215a

04 34 35 92 78
En savoir plus >

Doctorant(e), Autre

IGF Nord 215b

04 34 35 92 78
En savoir plus >

Chercheur CDD, Inserm

IGF Nord 215b

04 34 35 92 78
En savoir plus >

Doctorant(e), UM

IGF Nord 223

04 34 35 93 07
En savoir plus >

Doctorant(e), CNRS

IGF Nord 215a

04 34 35 93 07
En savoir plus >
Techniciens et ingénieurs CDD

IE CDD, CNRS

IGF Nord 221a

04 34 35 92 89
En savoir plus >

IE CDD, CNRS

IGF Nord 221a

04 34 35 93 07
En savoir plus >

IE CDD, CNRS

IGF Nord 216a

04 34 35 92 63
En savoir plus >

IE CDD, CNRS

IGF Nord 223

04 34 35 92 78
En savoir plus >

IE CDD, CNRS

IGF Nord 223

04 34 35 92 78
En savoir plus >

IECN CDD, CNRS

IGF Nord 209b

04 34 35 92 89
En savoir plus >
Stagiaires

Master 2, CNRS

IGF Nord 215b

04 34 35 92 78
En savoir plus >

Master 2, CNRS

IGF Nord 221a

04 34 35 93 07
En savoir plus >

Stagiaire, CNRS

IGF Nord 223

04 34 35 92 89
En savoir plus >
- Xu C, Zhou Y, Liu Y, Lin L, Liu P, Wang X, Xu Z, Pin JP*, Rondard P*, Liu J* (2024). Specific pharmacological and Gi/o protein coupling properties of native GPCRs in neurons. Nat Comm 2024 15(1) :1990. doi: 10.1038/s41467-024-46177-z. PMID: 38443355 * Co-corresponding author.
- Lecat-Guillet N, Quast RB, Liu H, Moeller TC, Rovira X, Soldevila S, Lamarque L, Trinquet E, Liu J, Pin JP, Rondard P*, Margeat E*. Concerted conformational changes control metabotropic glutamate receptor activity. Sci Adv 2023 9 (22) :eadf1378. doi: 10.1126/sciadv.adf1378. PMID: 37267369 * Co-corresponding author.
- Meng J, Xu C, Lafon PA, Roux S, Mathieu M, Zhou R, Scholler P, Blanc E, Becker JAJ, Le Merrer J, González-Maeso J, Chames P, Liu J*, Pin JP*, Rondard P*. Optical biosensors of native membrane protein complexes reveal a high proportion of mGlu heterodimers in the brain. Nat Chem Biol 2022, 18, 894-903. doi: 10.1038/s41589-022-01050-2. PMID: 35681029 * Co-corresponding author.
- Liu J, Tang H, Xu C, Zhou S, Zhu X, Li Y, Prézeau L, Xu T, Pin JP*, Rondard P*, Ji W*, Liu J* (2022) Biased signaling due to oligomerization of a G protein-coupled receptor. Nat Comm 2022 13, 6365. doi: 10.1038/s41467-022-34056-4. PMID: 36289206 * Co-corresponding author.
- Haubrich J, Font J, Goupil-Lamy A, Scholler P, Nevoltris D, Acher F, Chames P, Rondard P, Prézeau L*, Pin J-P*. A nanobody activating metabotropic glutamate receptor 4 discriminates between homo- and heterodimers. Proc Natl Acad Sci U S A 2021 118 (33):e2105848118. doi: 10.1073/pnas.2105848118. PMID: 34385321* Co-corresponding author.
- Cao AM, Quast RB, Fatemi F, Rondard P, Pin JP*, Margeat E* (2021) Allosteric modulators enhance agonist efficacy by increasing the residence time of a GPCR in the active state. Nat Comm 2021 12 (1):5426. doi: 10.1038/s41467-021-25620-5. PMID: 34521824* Co-corresponding author.
- Liu H, Yi P, Zhao W, Wu Y, Acher F, Pin JP*, Liu J*, Rondard P. Illuminating the allosteric modulation of the calcium sensing receptor. Proc Natl Acad Sci U S A 2020 117 (35) 21711-21722. doi: 10.1073/pnas.1922231117. PMID: 32817431 * Co-corresponding author.
- Xue L, Sun Q, Zhao H, Rovira X, Gai S, He Q, Pin JP*, Liu J*, Rondard P. Rearrangement of the transmembrane domain interfaces associated with the activation of a GPCR hetero-oligomer. Nat Commun 2019 10, 2765. doi: 10.1038/s41467-019-10834-5. PMID: 31235691 * Co-corresponding author.
- Scholler P, Nevoltris D, De Blundel D, Bossi S, Moreno D, Rovira X, Møller TC, El-Moustaine D, Mathieu M, Blanc E, McLean H, Dupuis E, Mathis G, Trinquet E, Daniel H, Valjent E, Baty D, Chames P, Rondard P*, Pin JP*. Allosteric nanobodies uncover a role of hippocampal mGlu2 receptor homodimers in contextual fear consolidation. Nat Commun 2017 8 (1):1967. doi: 10.1038/s41467-017-01489-1. PMID: 29213077 * Co-corresponding author.
- Scholler P, Moreno D, Lecat-Guillet N, Doumazane E, Monnier C, Charrier-Savournin F, Fabre L, Chouvet C, Soldevila S, Lamarque L, Donsimoni G, Roux T, Zwier JM, Trinquet E, Rondard P*, Pin JP*. HTS-compatible FRET-based conformational sensors clarify membrane receptor activation. Nat Chem Biol 2017 13, 372-380. doi: 10.1038/nchembio.2286. PMID: 28135236 * Co-corresponding author

Développement de méthodes et d’outils pour étudier les RCPG
Responsable
Jean-Philippe PIN
En savoir plus
Complexes de récepteurs mGlu et leur dynamique en environnement natif
Responsable
Laurent PREZEAU
En savoir plus
Nanobodies ciblant les récepteurs mGlu : immunothérapie innovante pour le traitement des maladies du cerveau
Responsable
Philippe RONDARD
En savoir plus
Revvity Cisbio
Codolet, France
Emmanuel Margeat
Centre de Biologie Structurale (CBS), Montpellier, France
Francine Acher
Université Paris Cité, Paris, France
Patrick Chames
Aix-Marseille Université, France
Jianfeng Liu
Huazhong University of Science and Technology (HUST), Wuhan, China
Amadeu Llebaria
University of Barcelona, Barcelona, Spain

Doctorants
• Alexandre Bouyssou (Genentech, USA)
• Laetitia Comps-Agrar (Genentech, USA)
• Mélanie Da Silva
• Damien Maurel
• Carine Monnier
• Mathieu Oosterlaken
• Marie-Laure Rives
• Pauline Scholler (Revvity)
Post-doctorants
• Fanny Dubois
• Driss El Moustaine
• Nathalie Lecat-Guillet (Revvity)
• Oualid Sbai
• Li Xue (Shanghai Jiao Tong University School of Medicine, Shanghai, China)
Ingénieurs
• Emilie Blanc
• Michaël Mathieu (Revvity)
• Jessica Monnic (Mabqi)
• Roxane Perrin
• Salomé Roux



 IGF Nord 223
IGF Nord 223 04 34 35 92 89
04 34 35 92 89
 IGF Nord 209b
IGF Nord 209b 04 34 35 92 78
04 34 35 92 78
 IGF Nord 223
IGF Nord 223 04 34 35 92 89
04 34 35 92 89
 IGF Nord 221a
IGF Nord 221a 04 34 35 93 07
04 34 35 93 07
 IGF Nord 221a
IGF Nord 221a 04 34 35 93 07
04 34 35 93 07
 IGF Nord 219
IGF Nord 219 04 34 35 93 13
04 34 35 93 13
 IGF Nord 221a
IGF Nord 221a 04 34 35 93 07
04 34 35 93 07
 IGF Nord 223
IGF Nord 223 04 34 35 93 07
04 34 35 93 07
 IGF Nord 215a
IGF Nord 215a 04 34 35 93 07
04 34 35 93 07
 IGF Nord 221a
IGF Nord 221a 04 34 35 93 07
04 34 35 93 07
 IGF Nord 223
IGF Nord 223 04 34 35 92 78
04 34 35 92 78
 IGF Nord 221a
IGF Nord 221a 04 34 35 92 78
04 34 35 92 78
 IGF Nord 209b
IGF Nord 209b 04 34 35 93 07
04 34 35 93 07
 IGF Nord 209b
IGF Nord 209b 04 34 35 92 89
04 34 35 92 89
 IGF Nord 223
IGF Nord 223 04 34 35 92 89
04 34 35 92 89
 IGF Nord 216a
IGF Nord 216a 04 34 35 92 63
04 34 35 92 63
 IGF Nord 215a
IGF Nord 215a 04 34 35 92 78
04 34 35 92 78
 IGF Nord 215b
IGF Nord 215b 04 34 35 92 78
04 34 35 92 78
 IGF Nord 215b
IGF Nord 215b 04 34 35 92 78
04 34 35 92 78
 IGF Nord 223
IGF Nord 223 04 34 35 93 07
04 34 35 93 07
 IGF Nord 215a
IGF Nord 215a 04 34 35 93 07
04 34 35 93 07
 IGF Nord 221a
IGF Nord 221a 04 34 35 92 89
04 34 35 92 89
 IGF Nord 221a
IGF Nord 221a 04 34 35 93 07
04 34 35 93 07
 IGF Nord 216a
IGF Nord 216a 04 34 35 92 63
04 34 35 92 63
 IGF Nord 223
IGF Nord 223 04 34 35 92 78
04 34 35 92 78
 IGF Nord 223
IGF Nord 223 04 34 35 92 78
04 34 35 92 78
 IGF Nord 209b
IGF Nord 209b 04 34 35 92 89
04 34 35 92 89
 IGF Nord 215b
IGF Nord 215b 04 34 35 92 78
04 34 35 92 78
 IGF Nord 221a
IGF Nord 221a 04 34 35 93 07
04 34 35 93 07
 IGF Nord 223
IGF Nord 223 04 34 35 92 89
04 34 35 92 89